Les ribosomes eucaryotes
Le ribosome est un complexe macromoléculaire qui catalyse la synthèse protéique à partir du décodage de l’information génétique contenue dans les ARN messagers (ARNm). C’est une machine moléculaire ribonucléoprotéique universelle, composée d’ARN ribosomiques (ARNr) et protéines ribosomiques (RP). Les ribosomes ont été découverts en 1955 par George E. Palade (Palade., 1955) avec l’observation de particules globulaires autour de la membrane du réticulum endoplasmique en microscopie électronique en transmission. Par la suite, de nombreuses études biochimiques et fonctionnelles ont été entreprises afin de mettre en lumière la composition et la fonction de ces complexes dans la synthèse protéique (Mcquillen et al., 1959 ; Palade 1975). Au cours des années 1980-90, la recherche sur la structure des ribosomes a rapidement progressée, grâce en particulier à la cryo microscopie électronique en transmission (cryo-EM) (Dubochet et al., 1988). Mais c’est au début des années 2000 que des études en cristallographie aux rayons X ont révélé la structure tridimensionnelle de ribosomes bactériens à l’échelle atomique. Ces travaux ont permis d’élucider la première structure des ribosomes procaryotes chez l’archaebactérie Haloarcula marismortui et la bactérie Thermus Thermophilus, à haute résolution (Ban et al., 2000 ; Yusupov et al., 2001). Ces modèles ont contribué notamment à une compréhension plus précise du rôle enzymatique de l’ARNr dans la synthèse protéique. En effet, la structure atomique de la grande sous-unité ribosomique 50S a mis en évidence que le site actif du ribosome, qui catalyse la réaction de synthèse des liaisons peptidiques, n’est en effet composé que par l’ARN ribosomique (Nissen, 2000 ; BAN, 2000 ; Muth, 2000). De ce fait, le ribosome s’est révélé être un véritable ribozyme.
La structure et la composition des ribosomes eucaryotes
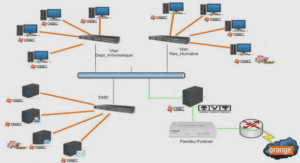
Les ribosomes sont composés de deux sous-unités de tailles et de morphologies distinctes, appelées communément petite et grande sous-unités. Chez les eucaryotes, la petite sous-unité est généralement nommée 40S (S, pour le coefficient de sédimentation Svedberg) et la grande sous-unité 60S (Figure 1). Le ribosome eucaryote comprend quatre ARNr et environ 80 protéines ribosomiques. Ainsi chez la levure Saccharomyces cerevisiae, la petite sous-unité est formée de l’ARNr 18S et de 33 protéines ribosomiques appelées RPS (Ribosomal Protein of the Small subunit). La grande sous-unité 60S est composée de trois ARNr dénommés 5S, 5.8S et 25S associés à 47 protéines nommées RPL (Ribosomal Protein of the large Subunit) (Ben-Shem et al., 2011 ; woolford et al., 2013). Chez l’Homme, la composition est similaire, seule change la taille du l’ARNr le plus grand appelé 28S (Anger et al., 2013 ; Khatter et al., 2015). La petite sous-unité constitue la plateforme de lecture du code génétique à travers l’appariement correct des ARN de transfert (ARNt) sur les codons de l’ARNm.
Elle est de forme allongée et possède 5 domaines caractéristiques : la tête, le bec, la plateforme, le corps et les pieds. La grande sous-unité 60S assure la synthèse des liaisons polypeptidiques entre les acides aminés durant la traduction par le biais de son domaine catalytique peptidyl-transférase. Elle est de forme globulaire et se caractérise par la présence d’un domaine central associé à trois protubérances : la protubérance centrale, les tiges P et L1.
Malgré le grand nombre des protéines ribosomiques, c’est l’ARNr qui demeure majoritaire en masse dans les ribosomes. Par ailleurs, par son arrangement spatial, imposé par sa séquence nucléotidique et l’appariement des bases complémentaires, c’est lui qui constitue le squelette de la structure du ribosome. Cette structure permet d’établir des sites d’interaction spécifiques entre les sous-unités ribosomiques et les acteurs de la traduction, en particulier les ARN de transfert (ARNt) et les ARNm. Ainsi, à l’interface des deux sous-unités existent trois sites de fixation pour les ARNt porteurs des acides aminés pendant la traduction (Figure 2). A chaque étape de traduction, le site A (pour Aminoacyl-ARNt) est occupé par l’ARNt porteur de l’acide aminé en attente d’être lié à la chaîne polypeptidique ; le site P (pour Peptidyl-ARNt) est occupé par l’ARNt porteur de l’acide aminé lié à la chaîne polypeptidique en cours de synthèse ; enfin, le site E (pour Exit) permet la libération de l’ARNt désacétylé qui a livré son acide aminé. ZLa structure des ribosomes s’est complexifiée au cours de l’évolution (Figure 3). Les ribosomes eucaryotes incluent à la fois plus de protéines ribosomiques et des ARNr de plus grande taille. Ainsi la masse du ribosome bactérien 70S, composé de la petite sous-unité 30S et la grande sous-unité 50S, est d’environ 2,5 MDa contre 3,2 MDa pour le ribosome 80S des eucaryotes unicellulaires et 4,3 MDa pour le ribosome 80S des eucaryotes supérieurs (Tableau 1). Les domaines supplémentaires sur les ARNr eucaryotes sont appelés segments d’extension. Leur allongement chez les mammifères pose la question de leurs rôles dans l’environnement complexe des cellules eucaryotes (Angers et al., 2013 ; Klinge et al., 2012).
Du fait de leur complexité compositionnelle plus grande, la structure 3D des ribosomes eucaryotes a été élucidée de manière plus tardive. C’est en 2010 qu’a été publiée la structure du ribosome de levure à haute résolution (4,15 Å) obtenue par cristallographie aux rayons X (BenShem et al., 2010). Un an plus tard, une structure à une résolution de 3,0 Å a précisé les relations entre les protéines ribosomiques et l’ARNr (Ben-shem et al., 2011). Enfin, concernant le ribosome humain, deux structures déterminées en 2013 (5,4-6 Å) puis en 2015 à l’échelle atomique (3 Å) par cryo-EM ont abouti à une cartographie complète de cette machinerie moléculaire ouvrant le champ d’étude à d’autres applications. En effet ces résultats pourraient aider à comprendre les effets des antibiotiques sur ces complexes et permettre de développer de nouveaux traitements contre certaines maladies liées aux ribosomes (Anger et al., 2013 ; Khatter et al., 2015).
La biogènese des ribosomes eucaryotes
L’assemblage des ribosomes eucaryotes est un processus complexe qui représente l’activité majeure de toute cellule en croissance. Chez les eucaryotes, ce processus est compartimenté : il démarre dans le noyau, où la transcription des gènes ribosomiques entraine la formation du nucléole; il se poursuit dans le nucléoplasme et s’achève dans le cytoplasme après export nucléaire des sous-unités ribosomiques en formation ou pré-ribosomes. La synthèse des ribosomes nécessite un grand nombre d’étapes de maturation successives et implique plusieurs processus : la transcription de l’ADN ribosomique (ADNr), le clivage et le repliement des ARNr, l’assemblage de l’ARNr avec les protéines ribosomiques, l’export des sous-unités ribosomiques vers le cytoplasme où se déroulent les dernières étapes de maturations. La biogenèse des ribosomes eucaryotes a été très étudiée chez la levure Saccharomyces cerevisiae, qui est un modèle facile à manipuler d’un point de vue génétique. Chez cet organisme, en phase exponentielle de croissance, la transcription des gènes ribosomiques équivaut à 60% de l’activité transcriptionnelle totale et environ 2000 ribosomes sont produits par minute (Warner, 1999). Ainsi, la majeure partie de l’activité métabolique des cellules en prolifération est dédiée à la biogenèse des ribosomes. Les travaux chez la levure ont mis en évidence la participation de centaines de facteurs en trans, protéines et particules RNP, dans la synthèse des ribosomes (Henras et al., 2008 ; 2015). Ces acteurs-clés sont seulement associés aux particules en cours de maturation et absents des sous unités matures. Ces protéines seront nommées co-facteurs de maturation (CFM) dans la suite du manuscrit de thèse. La plus grande partie de ce processus se déroule dans le noyau, mais les particules pré-ribosomiques exportées dans le cytoplasme ne sont pas encore compétentes pour la traduction et doivent subir d’ultimes étapes de maturation. A l’instar des autres processus de maturation des ARN impliqués dans la traduction, le confinement de la maturation dans le noyau évite les interactions prématurées des ARN ribosomiques (ARNr) avec les acteurs de la traduction. La synthèse des ribosomes est un mécanisme qui semble globalement conservé chez les eucaryotes, mais un nombre croissant d’études a montré qu’elle s’est encore complexifiée chez les plantes ou les animaux. En combinant les ARNr et les protéines ribosomiques de la bactérie Escherichia coli dans un ordre précis, il est possible de provoquer l’auto-assemblage de ribosomes procaryotes matures et fonctionnels in vitro (Nomura, 1970). Ceci est impossible avec des ribosomes eucaryotes, ce qui souligne la complexité plus importante de la structure des sous unités et des mécanismes de leur synthèse.
L’assemblage des ribosomes commence de manière co-transcriptionnelle dans le nucléole. La transcription des gènes ribosomiques s’opère grâce à l’ARNr polymérase I (ARN POL I) et donne naissance à un long précurseur polycistronique (pré-ARNr primaire) contenant la séquence des ARNr 18S, 28/25SS et 5,8S (Figure 4 et Figure 6). La production des ribosomes requiert également l’intervention cordonnée de deux autres ARN POL : la transcription des ARNm des protéines ribosomiques est assurée par l’ARN POL II et la production de l’ARNr 5S est effectuée par l’ARN POL III. Dans le nucléole, le long précurseur des ARNr polycistronique, s’associe à la majorité des RP, des snoRNP ainsi que des co facteurs de maturation afin de former une particule nommée 90S. Ce long transcrit subit des modifications chimiques sur des nucléotides spécifiques telles que la méthylation en position 2′ des riboses ou encore l’isomérisation d’uridines en pseudo-uridines (pseudouridylation) par des snoRNPs. Ces modifications sont guidées par de petits ARN nucléolaires (les snoARN) qui s’hybrident au niveau des nucléotides à modifier. Les séquences flanquantes des ARN ribosomiques dans le pré-ARNr sont par ailleurs excisées par l’action concertée d’endo- et d’exonucléases, afin de générer un précurseur de la petite sous-unité ribosomique (pré-40S) et un précurseur de la grande sous-unité ribosomique (pré-60S) (Figure 4). Ces deux particules pré-ribosomiques empruntent ensuite des voies de maturation indépendantes dans le noyau et le nucléoplasme. Après transport du nucléoplasme vers le cytoplasme à travers le complexe de pore nucléaire (CPN), les particules pré ribosomiques subissent les étapes finales de leur maturation qui permet leur participation à la traduction. En ce qui concerne les particules pré-40S, les grandes étapes de maturation cytoplasmique se caractérisent par l’association des dernières protéines ribosomiques, la libération séquentielle des co-facteurs de maturation qui accompagnent la particule dans le cytoplasme, et le clivage à l’extrémité 3’ de l’ARNr 18S médié par l’activité endonucléolytique du co-facteur de maturation Nob1. Chez la levure, ces dernières étapes impliquent également une association transitoire entre les particules pré-40S et la grande sous-unité 60S formant ainsi des particules « pseudo-80S » potentiellement impliquées dans une étape de contrôle-qualité. Ces étapes de maturation cytoplasmique sont globalement comparables entre l’Homme et la levure, mais des différences soulignent la complexité accrue de ce processus au cours de l’évolution. Par la suite, je m’attacherai à décrire la biogenèse de la petite sous-unité ribosomique eucaryote qui a fait l’objet de mon travail de thèse.
Les acteurs de l’assemblage de la petite sous-unité ribosomique 40S
La maturation de l’ARNr : Du pré-ARNr primaire à l’ARNr 18S
La séquence de l’ARNr 18S (composant de la petite sous-unité 40S) comprise dans le pré-ARNr polycistronique, est délimitée par l’extrémité 5’ flanquante (5’ ETS) et l’espaceur interne ITS1 (Figure 6). La formation de l’ARNr 18S mature nécessite donc l’élimination de ces deux séquences. Pour ce faire, trois étapes successives sont requises chez la levure : la maturation progressive de l’extrémité 5’-ETS pour former l’extrémité 5’ de l’ARNr ; le clivage endonucléolytique dans l’espaceur ITS1 ; le clivage de l’extrémité 3’ au site D par l’endonucléase Nob1 dans le cytoplasme, afin de former l’extrémité 3’ mature de l’ARNr 18S. Chez l’Homme, la maturation de l’extrémité 3′ du 18S fait également intervenir des exonucléases 3′-5′ (Carron et al., 2011; Preti et al, 2013; Sloan et al., 2013; Montellese et al., 2018).
Les étapes précoces de la maturation de l’ARNr 18S prennent place dans une particule pré-ribosomique, dite particule 90S ou SSU processome, qui s’assemble cotranscriptionnellement et dans laquelle on trouve la snoRNP U3 et plus de 72 co facteurs de maturation.
La composition de cette particule de 2,2 MDa a été élucidée grâce à des approches biochimiques et structurales telles que la purification d’affinité couplée à la spectrométrie de masse et à la cryo-EM (Krogan et al., 2004 ; Grandi et al., 2002 ; Kornprobst et al., 2016 ; Cheng et al., 2017). L’assemblage du SSU processome fait intervenir l’association séquentielle de plusieurs modules appelés complexes UTP (pour U three proteins), comme UTP-A, UTP-B et snoRNP U3 au pré-ARNr. Ce précurseur est également composé de l’ARNr 5S associé à un complexe protéique (Zhang et al., 2007). Les études sur la maturation du pré-ARNr 35S, chez la levure S. cerevisiae, montre que chez cet organisme, en phase exponentielle de croissance, 70% des transcrits primaires sont clivés de manière co-transcriptionnelle dans l’ITS1 contre 30% de façon post-transcriptionnelle (Fernandez et al., 2015). Cela a été observé en microscopie électronique en transmission (MET) par étalement de gènes ribosomiques en transcription, ou arbres de Miller (Miller et al., 1969 ; Osheim et al., 2004) (Figure 5). D’autres études suggèrent que ce même clivage est principalement posttranscriptionnel chez les vertébrés (Mougey et al., 1993). Les étapes de maturation du pré-ARNr primaire sont relativement conservées entre la levure et l’Homme.
|
Table des matières
I. INTRODUCTION
I.A Les ribosomes eucaryotes
I.A.1 La structure et la composition des ribosomes eucaryotes
I.A.2 La biogènese des ribosomes eucaryotes
I.B Les acteurs de l’assemblage de la petite sous-unité ribosomique 40S
I.B.1 La maturation de l’ARNr : Du pré-ARNr primaire à l’ARNr 18S
I.B.1.1 Maturation de l’extrémité 5’-ETS de l’ARNr 18S
I.B.1.2 Maturation de l’extrémité 3’ de l’ARNr 18S
I.B.1.3 Les modifications post-transcriptionnelles de l’ARNr
I.B.2 L’assemblage des protéines ribosomiques (RP)
I.B.3 Le rôle des co-facteurs de maturation (CFM)
I.B.3.1 Activité enzymatique des CFM
I.C Etapes de la maturation des particules pré-40S
I.C.1 Export nucléo-cytoplasmique des particules pré-40S eucaryotes
I.C.2 Etapes de maturation cytoplasmique des particules pré-40S de levure
I.C.3 Les étapes de maturation cytoplasmique des particules pré-40S de l’Homme
I.D Apport de la cryo-EM dans l’étude des ribosomes
I.D.1 Etude structurale des ribosomes matures
I.D.2 Etude structurale des particules pré-40S cytoplasmiques
I.D.3 Positionnement et rôle des CFM cytoplasmiques impliqués dans l’assemblage de la petite sous-unité 40S, chez la levure
I.D.4 Positionnement et rôle des CFM cytoplasmiques impliqués dans l’assemblage de la petite sous-unité 40S, chez l’Homme
I.E Contexte, problématique et objectifs de la thèse
II. MATERIELS ET METHODES
II.A. Purification des particules pré-ribosomiques pré-40S
II.A.1 Purification des particules pré-40S de levures Tsr1-FPZ
II.A.2 Particules pré-40S de levures : Tsr1-TAP rps20Δloop
II.A.3 Purification des particules pré-40S humaines RIO1(kd)-TAP
II.B Microscopie électronique en transmission
II.B.1 Grilles de microscopie électronique en transmission
II.B.2 Ionisation des grilles
II.B.3 Principes généraux
II.B.3.1 Source d’électrons
II.B.3.2 La colonne
II.B.3.3 Les lentilles électromagnétiques
II.B.3.4 Détecteurs d’électrons
II.B.3.5 L’Intéractions des électrons avec l’échantillon et formation d’image
II.B.3.6 Formation d’images
II.B.3.7 La fonction de transfert de contraste (CTF)
II.C Préparation et acquisition d’images de l’échantillon biologique
II.C.1 Préparation de l’échantillon
II.C.1.1 Préparation de l’échantillon pour la coloration négative
II.C.1.2 Préparation de l’échantillon pour la cryo-congélation
II.C.2 Acquisition des images en cryo-EM
II.D Analyse d’images
II.D.1 Principes généraux
II.D.2 Le programme RELION 2.1.0
II.D.2.1 Pré-traitement
II.D.2.2 La classification 2D
II.D.2.3 La classification 3D
II.D.2.4 Auto-raffinement
II.D.2.5 Post-traitement
II.D.2.6 Auto-raffinement et classification masqués avec ou sans soustraction du signal
II.D.3 Interprétation des cartes de densité : construction d’un modèle atomique
II.D.4 Les ressources informatiques
III. RESULTATS
III.1 Détermination de la structure de particules pré-40S cytoplasmiques de levures (Tsr1-FPZ)
III.1.A Purification des particules Tsr1-FPZ
III.1.B Analyse structurale des particules pré-40S Tsr1-FPZ par cryo-EM
III.1.B.1 Acquisition d’images au NeCEN
III.1.B.2 Acquisition d’images à l’ESRF
III.1.B.2.1 Analyse d’images par classification « globale »
III.1.B.2.2 Analyse d’images par classification localisée
III.1.C Discussion
III.1.D Perspectives
III.2 Détermination de la structure de particules pré-40S cytoplasmiques de levures (Delta-loop Rps20)
III.2.A Objectifs et résumé de l’article
III.2.B Article : Conformational proofreading of distant 40S subunit maturation events by a long-range communication Mechanism
III.3 Détermination de la structure de particules pré-40S cytoplasmiques humaines tardives (RIO1(kd)-TAP)
III.3.A Purification et analyse compositionnelle des particules RIO1(kd)-TAP
III.3.B Analyse structurale des particules pré-40S RIO1(kd)-TAP par Cryo-EM
III.3.B.1 Analyse du modèle « consensus »
III.3.B.2 Analyse par classification 3D globale
III.3.B.3 Analyse par auto-raffinement et classification localisé
III.3.C Discussion
III.3.D Perspectives
IV. Conclusion générale