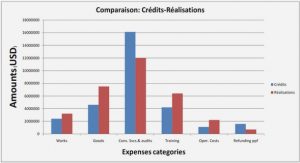
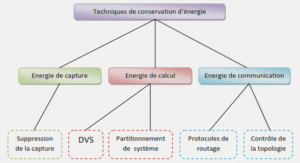
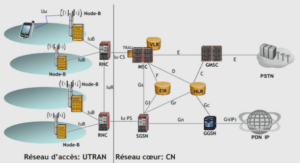
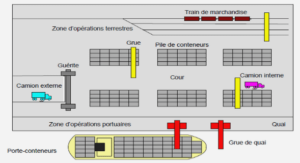
Culture, isolement et identification des souches de H. pylori
Un total de 8 biopsies gastriques a été réalisé chez des patients présentant des lésions macroscopiques, lors de l’endoscopie digestive, susceptibles de bénéficier de l’éradication de H. pylori, Deux biopsies antrales et 2 biopsies fundiques ont été fixées en formol tamponné à 10% pour le diagnostic histopathologique. Deux biopsies antrales et 2 biopsies fundiques, ont été placées dans de l’eau physiologique (NaCl à 9‰) pour le diagnostic microbiologique. Pour la culture bactériologique, les biopsies ont été broyées puis ensemencées sur une gélose Mueller Hinton additionnée de 10% de sang de cheval frais défibriné et une gélose Colombia supplémentée d’un cocktail antibiotique (Supplément sélectif pour Helicobacter pylori: SR0147, Oxoid). Les milieux ont été incubés en atmosphère microaérophile (5% O2, 10% CO2, 85% N2) à 37°C pendant un maximum de 12 j ours. L’identification microbiologique a été réalisée sur l’aspect des colonies, la morphologie des bactéries après coloration de Gram, la synthèse d’une oxydase, d’une catalase et d’une uréase .
Extraction de l’ADN génomique
Cinq extractions ont été menées parallèlement et indépendamment. Chaque extraction a été réalisée à partir d’une anse de 10µl, pleine de culture bactérienne, à l’aide du kit d’extraction QIAamp™ DNA Minikit (250) Cat. No 51306, ( Qiagen) de façon à obtenir 200 µl de solution d’ADN à la concentration de 15 à 50 µg/ml. Dix microlitres de chaque solution d’ADN ont été déposé s ur un ge l d’agarose à 1,5%. Après migration électrophorétique de 45mn à 120V, l’intensité de la bande a permis de vérifier la quantité d’ADN extrait. L’ADN extrait a été « poolé » (volume total : 1000 µl) puis dilué au 1/20e en vue des différentes amplifications .
Recherche du gène cagA, marqueur de la présence de cag-PAI (PCR cagA)
Les amorces CagA-F et CagA-R (Tableau VI) ont été utilisées, ainsi que les concentrations expérimentales finales suivantes: Tampon 1X Taq Eurobio sans MgCl2 (TrisHCl 10 m M, pH 9,0, K Cl 50 m M) ; 1,5mM de MgCl2 ; 0,5µM d’Amorces; 200 µM de désoxynucléique (A, T, C, G) à 1,25mM pour chaque nucléotide ; 1,5U de Taq polymérase ; et 1 µl d’ADN dilué au 1/20e (soit environ 50ng d’ADN) pour un volume total de 50µl. Les Amplifications ont été réalisées en utilisant un thermocycleur de type AB Applied Biosystems 2720 avec les paramètres suivants : 9 mn de pré-dénaturation à 94°C suivie de 40 cycles de [30s à 94°C ; 45s à 50°C ; 45s à 72°C] et une incubation finale à 72°C pendant 5 mn . Les amplicons ont été révélés par une lecture sous UV après la migration éléctrophorétique . Une confirmation de l’absence du gène cagA a été réalisée par la PCR ES en cas de non amplification de ce gène.
Confirmation de l’absence du gène cagA (PCR ES)
Cette PCR est appliquée sur les souches dont le gène cagA n’a pas été détecté par la PCR CagA. Les amorces CagA-2 et CagA-25 ont été utilisées. Ce sont des amorces spécifiques aux régions bordants le cag-PAI et vont donc permettre d’avoir une amplification chez les souches à cagA négatif. Les concentrations expérimentales suivantes ont été utilisées : Tampon 1X Taq Eurobio sans Mgcl2 (Tris-HCl 10 mM, pH 9,0, KCl 50 mM) ; 1,5mM de Mgcl2 ; 0,5µM d’Amorces ; 200 µM de désoxynucléique (A, T, C, G) à 1,25mM pour chaque nucléotide ; 1,5U de Taq polymérase ; et 1 µ l d’ADN dilué au 1/20e (soit environ 50ng d’ADN) pour un volume total de 50µl. Les Amplifications ont été réalisées en utilisant un thermocycleur de type AB Applied Biosystems 2720 avec les paramètres suivants : 5mn de pré dénaturation à 94°C pour activer la Taq polymérase suivie de 35 cycles de [1mn à 94°C ; 1mn à 57°C ; 1mn à 72°C] et une incubation finale à 72°C pendant 5mn .
Etude de la diversité de la région 3’ du gène cagA
La PCR EPIYA a été appliquée sur les souches ayant le gène cag A Les amorces CagA-2530S et CagA-3000AS ont été utilisées. Les concentrations expérimentales suivantes ont été utilisées : Tampon 1X Taq Eurobio sans Mgcl2 (Tris-HCl 10 mM, pH 9,0, K Cl 50 mM) ; 1,5mM de Mgcl2 ; 0,5µM d’Amorces ; 200 µM de désoxynucleique (A, T, C, G) à 1,25mM pour chaque nucléotide ; 1,5U de Taq polymérase ; de l’eau Eurobio (GAUEU00F-01) ; et environ 50 ng d’ADN pour un volume total de 50µl. Les Amplifications ont été réalisées en utilisant un thermocycleur de type AB Applied Biosystems 2720 avec les paramètres suivants : 5mn de pré dénaturation à 94°C suivie de 35 cycles de [5 mn à 94°C ; 30s à 94°C ; 45s à 50°C ; 45s à 72°C] et une incubation finale à 72°C pendant 5 mn . La révélation des produits de la PCR a ét é faite sous UV après la migration éléctrophorétique .
Amplification de la région 3’ du gène cagA
En se basant sur les séquences peptidiques des protéines CagA présentes dans la base GenBank, des séquences conservées bordant la région 3’ de la protéine CagA contenant les motifs EPIYA ont été identifiées. Des amorces dégénérées ont été synthétisées (position 582 453 à 582 977 du génome de la souche H. pylori 26695) pour l’amplification de cette région (Panayotopoulou, et al., 2007). Les amorces 2530S et 3000AS ont été utilisées. Les Amplifications ont été réalisées en utilisant un thermocycleur de type AB Applied Biosystems 2720 avec les paramètres suivants : 5mn de pré dénaturation à 94°C suivie de 35 cycles de [5 mn à 94°C; 30s à 94°C ; 45s à 50°C ; 45s à 72°C] et une incubation finale à 72°C pendant 5 mn.
Séquençage des amplicons
Après contrôle de la taille et de la concentration des produits PCR (minimum 20 ng/µl), 2 µl des produits d’amplification purifiés ont ensuite été séquencés à l’aide du kit Big DyeTM Terminator (V.1.1.). L’ensemble des réactions de séquence ont été réalisées à la Plateforme technique de l’Institut Pasteur de Paris.
Identification des motifs EPIYA
L’alignement multiple des séquences protéiques générées a été réalisé par le logiciel Clustal W.
Construction d’un arbre phylogénétique
Les étapes suivantes ont permis sa création :
– Chercher dans la banque de données de séquences Genbank les séquences connues similaires par blast avec la séquence protéique de la souche 26695 (position 582 453 à 582 977 du génome séquencée de la souche H. pylori 26695),
– Réaliser l’alignement multiple des séquences protéiques par le logiciel Clustal W,
– Construire l’arbre phylogénétique par le logiciel Applied Math en utilisant la méthode de Neighbor Joining.
|
Table des matières
Introduction
Chapitre. 1 : GENERALITES
Chapitre. 2 : MATERIELS ET METHODES
2.1. Inclusion des patients et isolement des souches
2.2. Culture, Isolement et Identification des souches de H. pylori
2.3. Extraction de l’ADN génomique
2.4. Etude de l’îlot de pathogénicité cag (cag-PAI)
2.4.1. Procédure moléculaire
2.4.2. Recherche de cagA, marqueur de la présence de cag-PAI (PCR CagA)
2.4.3. Confirmation de l’absence de cag-PAI (PCR-ES)
2.4.4. Etude de la diversité de la région 3’ du gène cagA
2.4.4.1. Amplification de la région 3’ du gène cagA
2.4.4.2. Séquençage des amplicons
2.4.4.3. Identification des motifs EPIYA
2.4.4.4. Construction d’un arbre phylogénétique
2.5. Etude de la clonalité des souches de H. pylori isolées chez un même Patient par RAPD
2.5.1. Isolement et subculture de 5 colonies des primocultures antrale et Fundique
2.5.2. Mise au point du RAPD
2.6. Sensibilité des souches
Chapitre. 3 : RESULTATS
3.1. Propriétés associées aux souches de H. pylori incluses dans l’étude
3.2. Amplification du gène cagA
3.3. Amplification de la région 3’du gène cagA codant pour les motifs EPIYA
3.3.1. Amplification de la région 3’ du gène cagA
3.3.2. Diversité du gène cagA, nombre et type de motifs EPIYA
3.3.3. Analyse phylogénétique
3.4. Etude de la clonalité des souches de H. pylori chez un même patient
3.5. Sensibilité des souches aux antibiotiques
Chapitre. 4 : DISCUSSION
Conclusion et Perspectives
Références bibliographiques
Annexes